حل چند معادله دیفرانسیل#
Heat Equation (معادله گرمایی)#
معادله گرمایی یکبعدی با ضریب پخش حرارتی \(\alpha = 0.4\) در دامنه \(x \in [0,1]\) و بازه زمانی \(t \in [0,1]\)
1. Boundary Conditions (شرایط مرزی)#
شرایط مرزی به صورت زیر در نظر گرفته شده (مانند میلهای که دو سر آن در دمای صفر درجه قرار گرفته است):
2. Initial Condition (شرط اولیه)#
توزیع دمای اولیه بهصورت تابع سینوسی با عدد مد \(n\) داده شده است:
3. Analytical Solution (حل تحلیلی)#
برای L = 1 و n = 1 پاسخ معادله دیفرانسیل به صورت زیر بیان میشود:
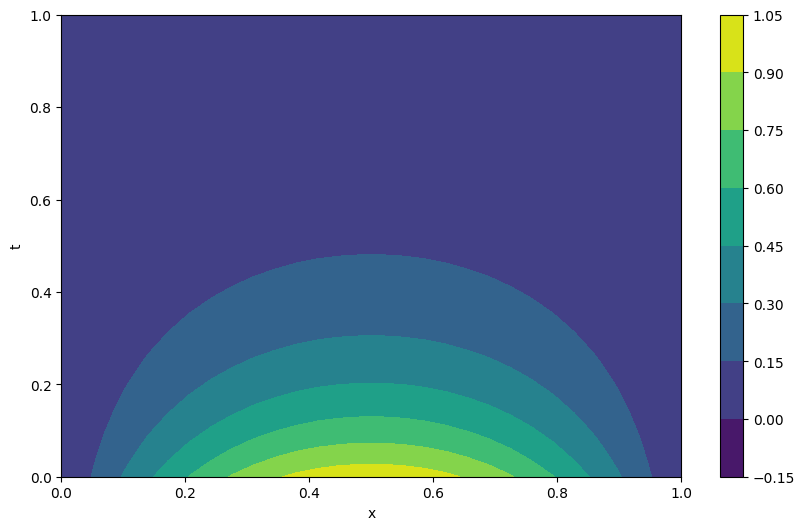
این جواب نشان میدهد که توزیع دما با گذر زمان بهصورت نمایی کاهش مییابد، در حالی که شکل فضایی آن به صورت سینوسی باقی میماند.
مشخصات ساختار شبکه عصبی مصنوعی#
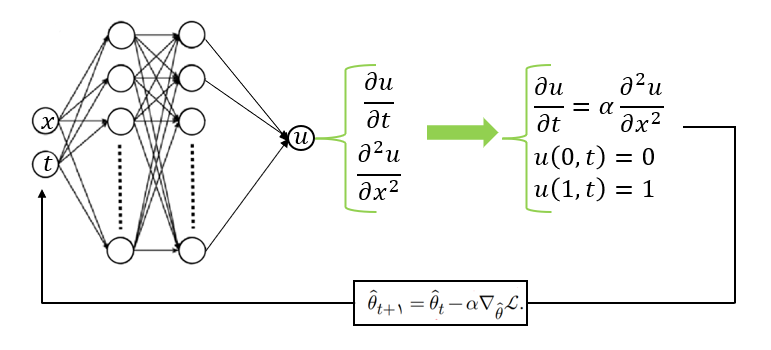
اندازه لایه ورودی: 2
تعداد لایه پنهان: 3
تعداد نورنهای لایه پنهان: 50
اندازه لایه خروجی: 1
تابع فعال ساز: tanh
فراخوانی کتابخانهها#
تابع torch.cuda.is_available() در کتابخانه Pytorch:#
این تابع بررسی میکند که آیا سیستم به یک GPU دسترسی دارد یا نه. اگر GPU توسط PyTorch قابل استفاده باشد، مقدار
Trueبرمیگرداند، در غیر این صورتFalse.
import torch
import torch.nn as nn
import matplotlib.pyplot as plt
from tqdm import trange
device = 'cuda' if torch.cuda.is_available() else 'cpu'
print(f"Your device is using {device}")
Your device is using cuda
ایجاد دادههای آموزشی#
تابع torch.meshgrid در PyTorch:#
تابعی است که دو بردار ورودی را گرفته و از آنها شبکهای دوبعدی از مختصات میسازد.
indexing ="ij": این دستور به این معنا است که ترتیب ماتریسها به صورتX[i,j]=x[i]وT[i,j]=t[j]است.indexing="xy": این دستور به این معنا است که ترتیب ماتریسها به صورتX[i,j]=x[j]وT[i,j]=t[i]است.
تابع ravel() در کتابخانه PyTorch:#
این تابع تمامی مقادیر ماتریس
XوTرا به صورت یک ماتریس تخت یا به صورت یک بردار تبدیل میکند.
تابع vstack() در کتابخانه PyTorch:#
این تابع دو تانسور را به صورت عمودی بهم میچسباند.
دستور to(device) در کتابخانه PyTorch:#
این دستور بسته به مقدار
deviceتانسورها را بر رویCPUیاGPUاجرا میکند.
domain = (0, 1)
n_train = 5
x = torch.linspace(domain[0], domain[1], n_train)
t = torch.linspace(domain[0], domain[1], n_train)
x.requires_grad = True
t.requires_grad = True
# print(x)
# print(t)
X, T = torch.meshgrid((x, t), indexing="ij")
# print(X)
# print(T)
# print(X.ravel())
# print(T.ravel())
points = torch.vstack([X.ravel(), T.ravel()])
# print(points)
points = points.T.to(device)
print(points)
tensor([[0.0000, 0.0000],
[0.0000, 0.2500],
[0.0000, 0.5000],
[0.0000, 0.7500],
[0.0000, 1.0000],
[0.2500, 0.0000],
[0.2500, 0.2500],
[0.2500, 0.5000],
[0.2500, 0.7500],
[0.2500, 1.0000],
[0.5000, 0.0000],
[0.5000, 0.2500],
[0.5000, 0.5000],
[0.5000, 0.7500],
[0.5000, 1.0000],
[0.7500, 0.0000],
[0.7500, 0.2500],
[0.7500, 0.5000],
[0.7500, 0.7500],
[0.7500, 1.0000],
[1.0000, 0.0000],
[1.0000, 0.2500],
[1.0000, 0.5000],
[1.0000, 0.7500],
[1.0000, 1.0000]], device='cuda:0', grad_fn=<ToCopyBackward0>)
ایجاد شبکه عصبی مصنوعی#
torch.manual_seed(42)
class NeuralNet(nn.Module):
def __init__(self, input_size, hidden_size, output_size):
super().__init__()
self.l1 = nn.Linear(input_size, hidden_size)
self.l2 = nn.Linear(hidden_size, hidden_size)
self.l3 = nn.Linear(hidden_size, hidden_size)
self.l4 = nn.Linear(hidden_size, output_size)
self.tanh = nn.Tanh()
def forward(self, x):
out = self.tanh(self.l1(x))
out = self.tanh(self.l2(out))
out = self.tanh(self.l3(out))
out = self.l4(out)
return out
input_size, hidden_size, output_size = 2, 50, 1
model = NeuralNet(input_size, hidden_size, output_size)
model.to(device)
NeuralNet(
(l1): Linear(in_features=2, out_features=50, bias=True)
(l2): Linear(in_features=50, out_features=50, bias=True)
(l3): Linear(in_features=50, out_features=50, bias=True)
(l4): Linear(in_features=50, out_features=1, bias=True)
(tanh): Tanh()
)
الگوریتم بهینه سازی#
learning_rate = 0.001
optimizer = torch.optim.Adam(model.parameters(), lr=learning_rate)
مشتقگیری از خروجیهای شبکه عصبی#
توضیح درباره خروجیهای torch.autograd.grad#
تابع torch.autograd.grad(outputs, inputs) گرادیان خروجیها را نسبت به ورودیها محاسبه میکند و یک لیست از تانسورها باز میگرداند. در اینجا، ما از [0] برای دسترسی به اولین (و تنها) عنصر این لیست استفاده میکنیم.
۱. وقتی از [:, 0:1] و [:, 1:2] استفاده میکنیم:#
[:, 0:1]: این عبارت مشتقuرا نسبت بهx(اولین ستون از ورودیها) محاسبه میکند.[:, 1:2]: این عبارت مشتقuرا نسبت بهt(دومین ستون از ورودیها) محاسبه میکند.
۲. وقتی از [:, :] استفاده نکنیم:#
اگر از [:, :] یا بدون هیچ زیر مجموعه انتخابی استفاده کنیم، تمام مقادیر گرادیانها (برای هر دو بعد x و t) را به عنوان یک تانسور بدون جدا کردن آنها دریافت خواهیم کرد. به عبارت دیگر، خروجی مشتق دوم شامل تمام مشتقات نسبت به تمام متغیرهای ورودی میشود.
$$
\frac{\partial^2 u}{\partial (\text{inputs})^2} =
=\begin{bmatrix} u_{xx} + u_{tx} & u_{xt} + u_{tt} \end{bmatrix}. $$
def grad(outputs, inputs):
return torch.autograd.grad(outputs, inputs, grad_outputs=torch.ones_like(outputs), create_graph=True)[0]
# points.requires_grad = True
print(f"inputs: {points}\n")
u = model(points)
print(f"outputs: {u}\n")
dudx = grad(u, points)[:, 0:1]
print(f"the derivative of u with respect to x:{dudx}\n")
d2udx2 = grad(dudx, points)[:, 0:1]
print(f"the second derivative of u with respect to x:{d2udx2}\n")
dudt = grad(u, points)[:, 1:2]
# print(f"the derivative of u with respect to t:{dudt}")
inputs: tensor([[0.0000, 0.0000],
[0.0000, 0.2500],
[0.0000, 0.5000],
[0.0000, 0.7500],
[0.0000, 1.0000],
[0.2500, 0.0000],
[0.2500, 0.2500],
[0.2500, 0.5000],
[0.2500, 0.7500],
[0.2500, 1.0000],
[0.5000, 0.0000],
[0.5000, 0.2500],
[0.5000, 0.5000],
[0.5000, 0.7500],
[0.5000, 1.0000],
[0.7500, 0.0000],
[0.7500, 0.2500],
[0.7500, 0.5000],
[0.7500, 0.7500],
[0.7500, 1.0000],
[1.0000, 0.0000],
[1.0000, 0.2500],
[1.0000, 0.5000],
[1.0000, 0.7500],
[1.0000, 1.0000]], device='cuda:0', grad_fn=<ToCopyBackward0>)
outputs: tensor([[0.0611],
[0.0672],
[0.0744],
[0.0825],
[0.0913],
[0.0569],
[0.0617],
[0.0678],
[0.0751],
[0.0835],
[0.0546],
[0.0582],
[0.0633],
[0.0698],
[0.0777],
[0.0541],
[0.0568],
[0.0611],
[0.0669],
[0.0742],
[0.0548],
[0.0570],
[0.0608],
[0.0661],
[0.0729]], device='cuda:0', grad_fn=<AddmmBackward0>)
the derivative of u with respect to x:tensor([[-0.0205],
[-0.0258],
[-0.0301],
[-0.0331],
[-0.0346],
[-0.0129],
[-0.0181],
[-0.0225],
[-0.0257],
[-0.0275],
[-0.0053],
[-0.0095],
[-0.0133],
[-0.0163],
[-0.0184],
[ 0.0007],
[-0.0019],
[-0.0046],
[-0.0071],
[-0.0093],
[ 0.0040],
[ 0.0030],
[ 0.0018],
[ 0.0001],
[-0.0018]], device='cuda:0', grad_fn=<SliceBackward0>)
the second derivative of u with respect to x:tensor([[0.0279],
[0.0261],
[0.0244],
[0.0231],
[0.0221],
[0.0318],
[0.0339],
[0.0350],
[0.0348],
[0.0335],
[0.0282],
[0.0337],
[0.0374],
[0.0388],
[0.0377],
[0.0189],
[0.0257],
[0.0311],
[0.0340],
[0.0342],
[0.0075],
[0.0135],
[0.0189],
[0.0227],
[0.0245]], device='cuda:0', grad_fn=<SliceBackward0>)
تابع هزینه مسئله معادله گرما#
در این مسئله معادلهی زیر را داشتیم:
بخشهای مختلف تابع هزینه (Loss Terms):#
L_phy: این بخش به معادله دیفرانسیل اصلی مربوط میشود
L_BC1: در شرایط مرزی ( x=0 ) مقدار تابع باید صفر باشد
L_BC2 : در شرایط مرزی ( x=1 ) مقدار تابع باید صفر باشد:
L_BCs : ترکیب دو شرط مرزی بالا برای نقاط ( x = 0 ) و ( x = 1 ):
L_IC : شرط اولیه برای زمان ( t = 0 ) به صورت تابع سینوسی زیر است:
🔺 در اینجا باید فقط نقاطی که در آن t = 0 هستند باید انتخاب شوند، یعنی نقاطی مانند (x, t=0) مجاز هستند، ولی نقاطی مانند (x, t=0.1) مجاز نیستند.
✅ نمونه مجاز: (0.5, 0)
❌ نمونه غیر مجاز: (0.5, 1)
تابع نهایی هزینه (Loss):
ایجاد نقاط مرزی#
points[:, 0] == 0: این دستور تمامی نقاطی را که مقدارxبرابر صفر است استخراج میکند. این تابع یک لیست به صورتBooleanبر میگرداند که در آن نقاطی که در شرط مورد نظر صدق میکنندTrueاست.points[:, 0] == 1): این دستور تمامی نقاطی را که مقدارxبرابر یک است استخراج میکند. این تابع یک لیست به صورتBooleanبر میگرداند که در آن نقاطی که در شرط مورد نظر صدق میکنندTrueاست.points[:, 1] == 0): این دستور تمامی نقاطی را که مقدارtبرابر صفر است استخراج میکند. این تابع یک لیست به صورتBooleanبر میگرداند که در آن نقاطی که در شرط مورد نظر صدق میکنندTrueاست.nonzero(as_tuple=True): این دستور اندیس نقاطی که شرایط برای آنها برقرار است را به صورتtupleبر میگرداندخروجی این دستور شامل دو موولفه است که دومین مولفه خالی است و اولین مولفه شامل لیستی از اندیسها است.
torch.cat([indices1, indices2]): این دستور برای چسباندن دو تانسور به کار میرود که اندیسهای دو مرز را با یکدیگر ترکیب میکند تا تمام نقاط مرزی به دست آید.
indices1 = (points[:, 0]==0).nonzero(as_tuple=True)[0]
indices2 = (points[:, 0]==1).nonzero(as_tuple=True)[0]
indices3 = (points[:, 1]==0).nonzero(as_tuple=True)[0]
indices12 = torch.cat([indices1, indices2])
def loss_fn(u, d2udx2, dudt, points, indices12, indices3, weights):
w1, w2, w3 = weights
L_phy = w1*torch.mean((dudt - 0.4*d2udx2)**2)
L_IC = w2*torch.mean((u[indices3] - torch.sin(torch.pi*points[indices3, 0:1]))**2)
L_BC = w3*torch.mean((u[indices12])**2)
loss = L_phy + L_BC + L_IC
return loss, L_phy, L_BC, L_IC
آموزش شبکه عصبی#
num_itrs = 2000
itr_show = 100
weights = (1, 1, 1)
L_total_history = []
L_phy_history = []
L_BC_history = []
L_IC_history = []
pbar = trange(num_itrs)
for itr in pbar:
u = model(points)
dudx = grad(u, points)[:, 0:1]
d2udx2 = grad(dudx, points)[:, 0:1]
dudt = grad(u, points)[:, 1:2]
loss, L_phy, L_BC, L_IC = loss_fn(u, d2udx2, dudt, points, indices12, indices3, weights)
loss.backward()
optimizer.step()
optimizer.zero_grad()
L_total_history.append(loss.item())
L_phy_history.append(L_phy.item())
L_BC_history.append(L_BC.item())
L_IC_history.append(L_IC.item())
pbar.set_postfix({'loss': loss.item()})
# if itr % itr_show == 0:
# print(f'iteration {itr}/{num_itrs}, loss = {loss.item():.6f}')
100%|████████████████████████████████████████████████████████████████| 2000/2000 [00:26<00:00, 74.18it/s, loss=1.21e-5]
بهرهبرداری از شبکه عصبی مصنوعی#
.view(n_test, n_test): از انجایی که دادههای خروجی در قالب یک بردار یک بعدی هستند برای رسم دو بعدی باید به شکل (n_test, n_test) بازآرایی کرد. اینکار باعث میشود دادههای در شبکهای مقادیرxوtقابل ترسیم باشند.plt.contourf(): ما تابع مدل را در صفحهی (x, t) محاسبه کردهایم. با استفاده ازplt.contourfمیتوانیم توزیع این تابع را در زمانها و مکانهای مختلف ببینیم.
n_test = 30
def exact_solution(points):
x, t = points[:, 0:1], points[:, 1:2]
return torch.exp(-0.4*(torch.pi**2)*t) * torch.sin(torch.pi*x)
t = torch.linspace(domain[0], domain[1], n_test)
x = torch.linspace(domain[0], domain[1], n_test)
X, T = torch.meshgrid((x, t), indexing="ij")
points = torch.vstack([X.ravel(), T.ravel()]).T.to(device)
predicted = model(points)
analytic_cal = exact_solution(points)
mse = torch.mean((predicted - analytic_cal)**2)
print(f"MSE error: {mse}")
predicted = predicted.view(n_test, n_test)
analytic_cal = analytic_cal.view(n_test, n_test)
plt.figure(figsize=(10, 6))
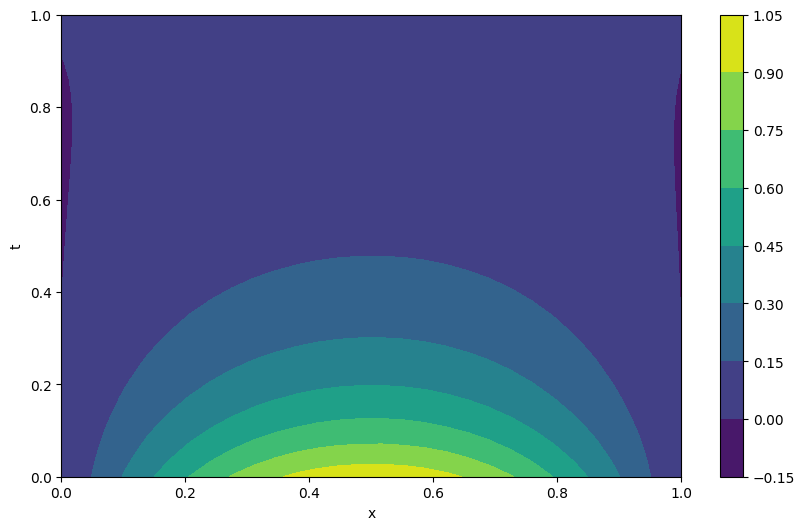
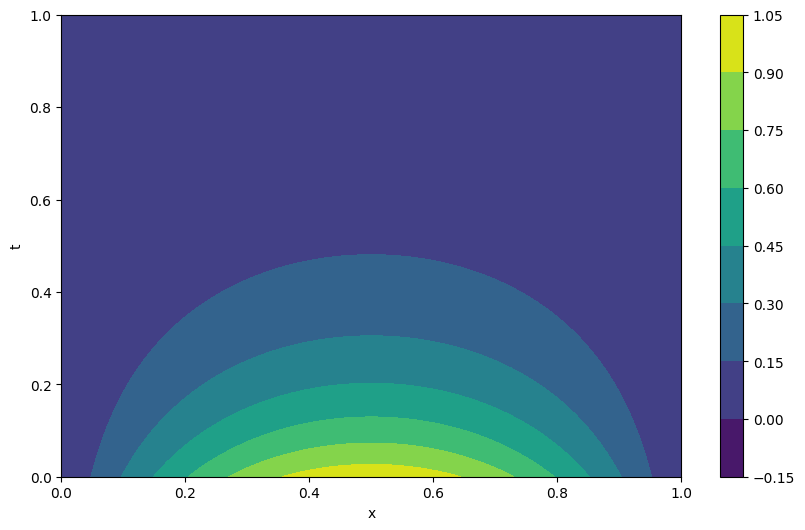
cp = plt.contourf(X.detach().numpy(), T.detach().numpy(), predicted.cpu().detach().numpy())
plt.colorbar(cp)
plt.xlabel('x')
plt.ylabel('t')
plt.show()
plt.figure(figsize=(10, 6))
cp = plt.contourf(X.detach().numpy(), T.detach().numpy(), analytic_cal.cpu().detach().numpy())
plt.colorbar(cp)
plt.xlabel('x')
plt.ylabel('t')
plt.show()
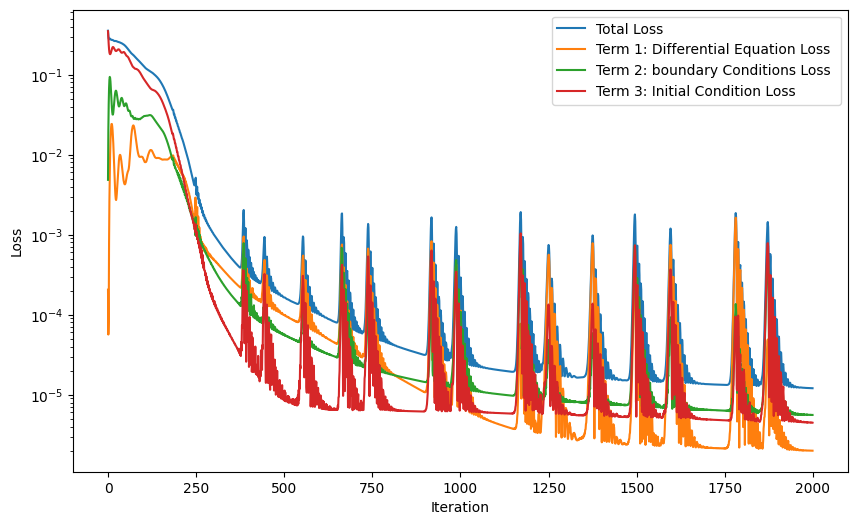
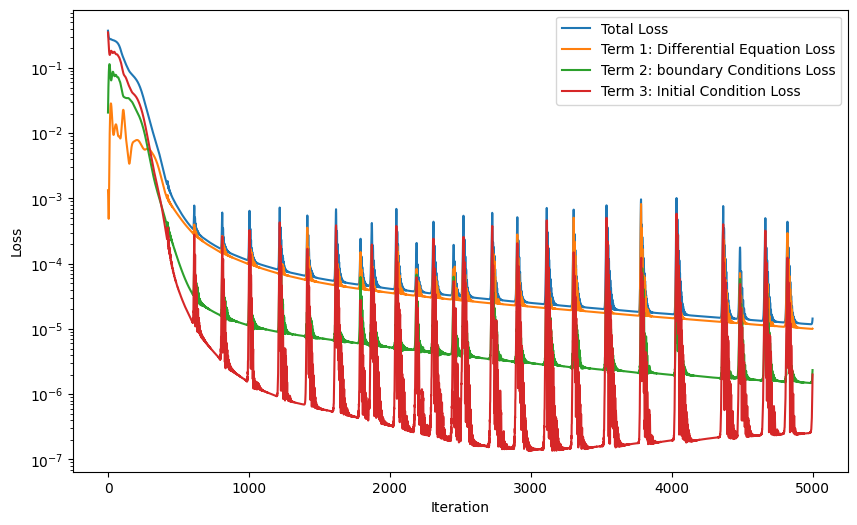
plt.figure(figsize=(10, 6))
plt.semilogy(L_total_history, label="Total Loss")
plt.semilogy(L_phy_history, label="Term 1: Differential Equation Loss")
plt.semilogy(L_BC_history, label="Term 2: boundary Conditions Loss ")
plt.semilogy(L_IC_history, label="Term 3: Initial Condition Loss")
plt.xlabel('Iteration')
plt.ylabel('Loss')
plt.legend()
plt.show()
MSE error: 1.2524047633633018e-05
پیادهسازی نهایی#
import torch
import torch.nn as nn
import matplotlib.pyplot as plt
from tqdm import trange
device = 'cuda' if torch.cuda.is_available() else 'cpu'
print(f"Your device is using {device}")
class NeuralNet(nn.Module):
def __init__(self, input_size, hidden_size, output_size):
super().__init__()
self.l1 = nn.Linear(input_size, hidden_size)
self.l2 = nn.Linear(hidden_size, hidden_size)
self.l3 = nn.Linear(hidden_size, hidden_size)
self.l4 = nn.Linear(hidden_size, output_size)
self.tanh = nn.Tanh()
def forward(self, x):
out = self.tanh(self.l1(x))
out = self.tanh(self.l2(out))
out = self.tanh(self.l3(out))
out = self.l4(out)
return out
class Trainer:
def __init__(self, model, optimizer, domain, weights):
self.model = model
self.optimizer = optimizer
self.domain = domain
self.weights = weights
self.L_total_history = []
self.L_phy_history = []
self.L_BC_history = []
self.L_IC_history = []
def exact_solution(self, points):
x, t = points[:, 0:1], points[:, 1:2]
return torch.exp(-0.4*(torch.pi**2)*t) * torch.sin(torch.pi*x)
def grad(self, outputs, inputs):
return torch.autograd.grad(outputs, inputs, grad_outputs=torch.ones_like(outputs), create_graph=True)[0]
def generate_data(self, n_data):
t = torch.linspace(self.domain[0], self.domain[1], n_data)
x = torch.linspace(self.domain[0], self.domain[1], n_data)
X, T = torch.meshgrid((x, t), indexing="ij")
data = torch.vstack([X.ravel(), T.ravel()]).T.to(device)
return X, T, data
def loss_fn(self, u, d2udx2, dudt, points, indices12, indices3, weights):
w1, w2, w3 = weights
L_phy = w1*torch.mean((dudt - 0.4*d2udx2)**2)
L_IC = w2*torch.mean((u[indices3] - torch.sin(torch.pi*points[indices3, 0:1]))**2)
L_BC = w3*torch.mean((u[indices12])**2)
loss = L_phy + L_BC + L_IC
return loss, L_phy, L_BC, L_IC
def train(self, n_train, num_itr, show_itr=False):
X, T, points = self.generate_data(n_train)
points.requires_grad = True
indices1 = (points[:, 0]==0).nonzero(as_tuple=True)[0]
indices2 = (points[:, 0]==1).nonzero(as_tuple=True)[0]
indices3 = (points[:, 1]==0).nonzero(as_tuple=True)[0]
indices12 = torch.cat([indices1, indices2])
pbar = trange(num_itr)
for itr in pbar:
u = model(points)
dudx = self.grad(u, points)[:, 0:1]
d2udx2 = self.grad(dudx, points)[:, 0:1]
dudt = self.grad(u, points)[:, 1:2]
loss, L_phy, L_BC, L_IC = self.loss_fn(u, d2udx2, dudt, points, indices12, indices3, weights)
loss.backward()
optimizer.step()
optimizer.zero_grad()
self.L_total_history.append(loss.item())
self.L_phy_history.append(L_phy.item())
self.L_BC_history.append(L_BC.item())
self.L_IC_history.append(L_IC.item())
if show_itr and itr % 100 == 0:
print(f'iteration {itr}/{num_itr}, loss = {loss.item():.6f}')
else:
pbar.set_postfix({'loss': loss.item()})
def evaluation(self, n_test):
X, T, points = self.generate_data(n_test)
predicted = self.model(points)
analytic_cal = self.exact_solution(points)
mse = torch.mean((predicted - analytic_cal)**2)
print(f"MSE error: {mse}")
predicted = predicted.view(n_test, n_test)
analytic_cal = analytic_cal.view(n_test, n_test)
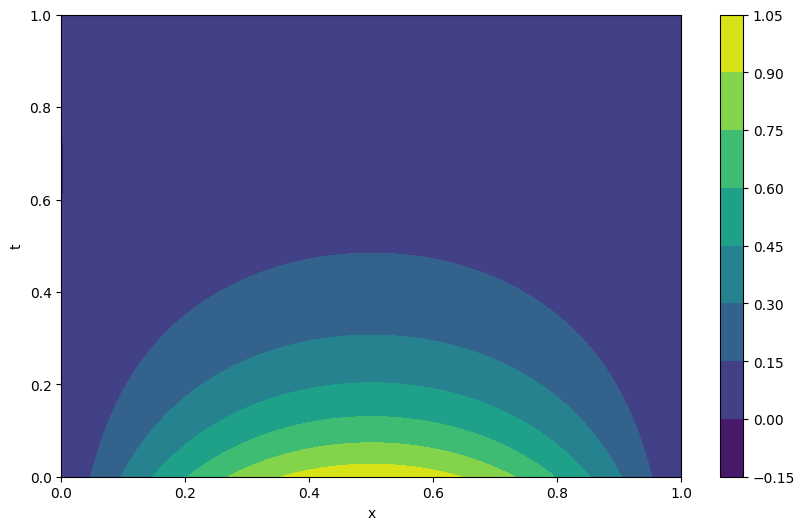
plt.figure(figsize=(10, 6))
cp = plt.contourf(X.detach().numpy(), T.detach().numpy(), predicted.cpu().detach().numpy())
plt.colorbar(cp)
plt.xlabel('x')
plt.ylabel('t')
plt.show()
plt.figure(figsize=(10, 6))
cp = plt.contourf(X.detach().numpy(), T.detach().numpy(), analytic_cal.cpu().detach().numpy())
plt.colorbar(cp)
plt.xlabel('x')
plt.ylabel('t')
plt.show()
plt.figure(figsize=(10, 6))
plt.semilogy(self.L_total_history, label="Total Loss")
plt.semilogy(self.L_phy_history, label="Term 1: Differential Equation Loss")
plt.semilogy(self.L_BC_history, label="Term 2: boundary Conditions Loss")
plt.semilogy(self.L_IC_history, label="Term 3: Initial Condition Loss")
plt.xlabel('Iteration')
plt.ylabel('Loss')
plt.legend()
plt.show()
Your device is using cuda
torch.manual_seed(42)
n_train, n_test, num_itr, itr_show = 30, 100, 5000, 1000
weights, domain = (1, 1, 1), (0, 1)
learning_rate = 0.001
input_size, hidden_size, output_size = 2, 30, 1
model = NeuralNet(input_size, hidden_size, output_size).to(device)
optimizer = torch.optim.Adam(model.parameters(), lr=learning_rate)
trainer = Trainer(model, optimizer, domain, weights)
trainer.train(n_train, num_itr, show_itr=False)
trainer.evaluation(n_test)
100%|████████████████████████████████████████████████████████████████| 5000/5000 [01:02<00:00, 80.62it/s, loss=1.44e-5]
MSE error: 2.189112137784832e-06
معادله لاپلاس بر روی یک دیسک#
حل معادله لاپلاس در ناحیهای به شکل دیسک واحد با استفاده از شبکههای عصبی:
شناخت مسئله#
1. شرط مرزی اول#
مقدار تابع \(u\) روی مرز دیسک (برای \(r=1\)) به صورت زیر داده شده است:
2. شرط مرزی دوم#
3. حل تحلیلی#
حل تحلیلی معادله لاپلاس برای این شرایط مرزی در دستگاه مختصات قطبی به صورت زیر است:
4. مشخصات ساختار شبکه عصبی مصنوعی#
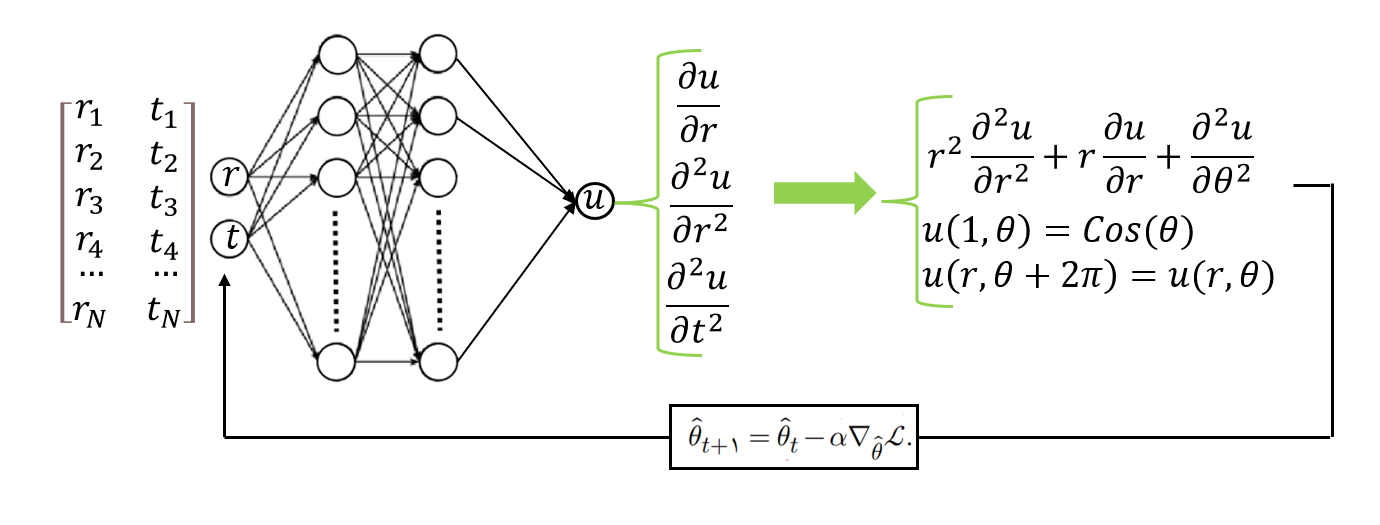
اندازه لایه ورودی: 2 (مختصات \(r\) و \(\theta\))
تعداد لایه پنهان: ۳
تعداد نورونهای لایه پنهان: ۵۰
اندازه لایه خروجی: ۱
تابع فعالساز: \(\tanh\)
فراخوانی کتابخانهها#
import torch
import torch.nn as nn
import matplotlib.pyplot as plt
from tqdm import trange
device = 'cuda' if torch.cuda.is_available() else 'cpu'
print(f"Your device is using {device}")
Your device is using cuda
ایجاد دادههای آموزشی برای آموزش شبکه عصبی مصنوعی#
domain1 = (0, 2*torch.pi) # theta
domain2 = (0, 1) # r
n_train = 30
t = torch.linspace(domain1[0], domain1[1], n_train)
r = torch.linspace(domain2[0], domain2[1], n_train)
R, T = torch.meshgrid((r, t), indexing="ij")
points = torch.vstack([R.ravel(), T.ravel()]).T.to(device)
ایجاد شبکه عصبی و الگوریتم بهینهسازی#
torch.manual_seed(42)
class NeuralNet(nn.Module):
def __init__(self, input_size, hidden_size, output_size):
super().__init__()
self.l1 = nn.Linear(input_size, hidden_size)
self.l2 = nn.Linear(hidden_size, hidden_size)
self.l3 = nn.Linear(hidden_size, hidden_size)
self.l4 = nn.Linear(hidden_size, output_size)
self.tanh = nn.Tanh()
def forward(self, x):
out = self.tanh(self.l1(x))
out = self.tanh(self.l2(out))
out = self.tanh(self.l3(out))
out = self.l4(out)
return out
input_size, hidden_size, output_size = 2, 50, 1
model = NeuralNet(input_size, hidden_size, output_size).to(device)
learning_rate = 0.001
optimizer = torch.optim.Adam(model.parameters(), lr=learning_rate)
مشتقگیری از خروجیهای شبکه عصبی#
def grad(outputs, inputs):
return torch.autograd.grad(outputs, inputs, grad_outputs=torch.ones_like(outputs), create_graph=True)[0]
points.requires_grad = True
u = model(points)
dudr = grad(u, points)[:, 0:1]
d2udr2 = grad(dudr, points)[:, 0:1]
dudt = grad(u, points)[:, 1:2]
d2udt2 = grad(dudt, points)[:, 1:2]
تابع هزینه برای حل معادله لاپلاس بر روی یک دیسک (در مختصات قطبی)#
در این مسئله، معادلهی لاپلاس در مختصات قطبی به صورت زیر داده شده است:
بخشهای مختلف تابع هزینه (Loss Terms):#
L_phy: این بخش به معادله دیفرانسیل اصلی مربوط میشود
L_BC1: در شرایط مرزی مقادیر تابع در (r=1) باید برابر \(cos(\theta)\) باشد:
L_BC2: در شرایط مرزی دورهای مقادیر تابع برای نقاطی که در آنها \(\theta=0\) و \(\theta=2\pi\) است باید با یکدیگر برابر باشد
تابع نهایی هزینه (Loss):
indices1 = (points[:, 0]==1).nonzero(as_tuple=True)[0].to(device)
indices2 = (points[:, 1]==2*torch.pi).nonzero(as_tuple=True)[0].to(device)
indices3 = (points[:, 1]==0).nonzero(as_tuple=True)[0].to(device)
def loss_fn(u, dudr, d2udr2, d2udt2, points, indices1, indices2, indices3, weights):
w1, w2, w3 = weights
L_phy = w1*torch.mean((points[:, 0:1]*dudr + (points[:, 0:1]**2)*d2udr2 + d2udt2)**2)
L_BC1 = w2*torch.mean((u[indices1] - torch.cos(points[indices1, 1:2]))**2)
L_BC2 = w3*torch.mean((u[indices2] - u[indices3])**2)
loss = L_phy + L_BC1 + L_BC2
return loss, L_phy, L_BC1, L_BC2
آموزش شبکه عصبی#
num_itrs = 2000
itr_show = 100
weights = (1, 1, 1)
L_total_history = []
L_phy_history = []
L_BC1_history = []
L_BC2_history = []
pbar = trange(num_itrs)
for itr in pbar:
u = model(points)
dudr = grad(u, points)[:, 0:1]
d2udr2 = grad(dudr, points)[:, 0:1]
dudt = grad(u, points)[:, 1:2]
d2udt2 = grad(dudt, points)[:, 1:2]
loss, L_phy, L_BC1, L_BC2 = loss_fn(u, dudr, d2udr2, d2udt2, points, indices1, indices2, indices3, weights)
loss.backward()
optimizer.step()
optimizer.zero_grad()
L_total_history.append(loss.item())
L_phy_history.append(L_phy.item())
L_BC1_history.append(L_BC1.item())
L_BC2_history.append(L_BC2.item())
pbar.set_postfix({'loss': loss.item()})
# if itr % itr_show == 0:
# print(f'iteration {itr}/{num_itrs}, loss = {loss.item():.6f}')
100%|█████████████████████████████████████████████████████████████████| 2000/2000 [00:33<00:00, 59.82it/s, loss=0.0012]
بهرهبرداری از شبکه عصبی مصنوعی#
n_test = 50
def exact_solution(points):
r, t = points[:, 0:1], points[:, 1:2]
return r*torch.cos(t)
t = torch.linspace(domain1[0], domain1[1], n_test)
r = torch.linspace(domain2[0], domain2[1], n_test)
R, T = torch.meshgrid((r, t), indexing="ij")
data = torch.vstack([R.ravel(), T.ravel()]).T
predicted = model(data.to(device))
analytic_cal = exact_solution(data).to(device)
mse = torch.mean((predicted - analytic_cal)**2)
print(f"MSE error: {mse}")
predicted = predicted.view(n_test, n_test)
analytic_cal = analytic_cal.view(n_test, n_test)
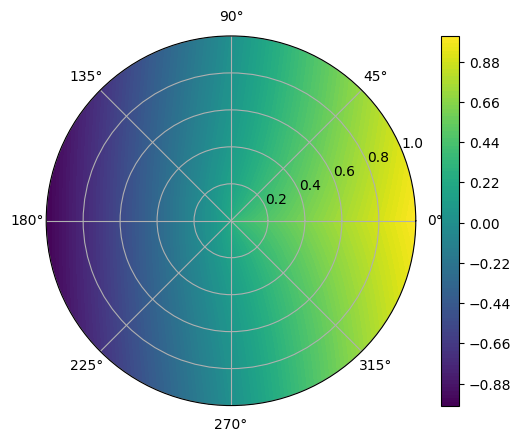
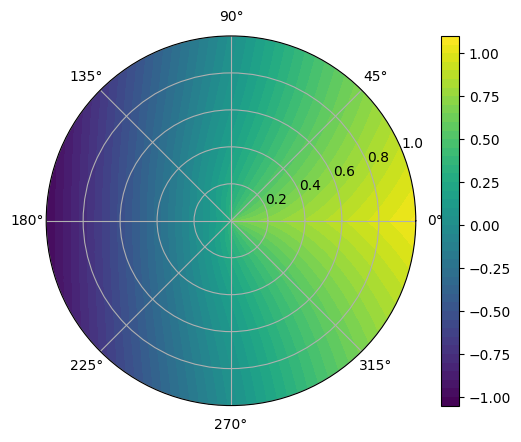
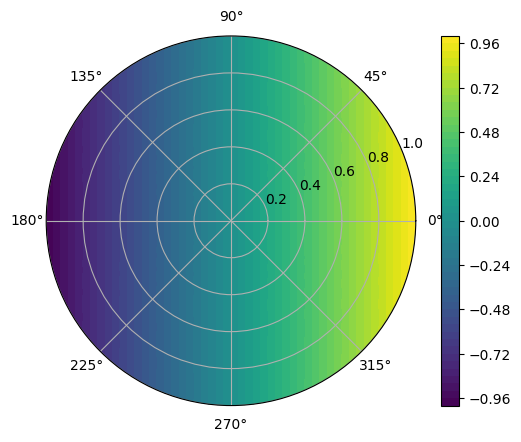
fig = plt.figure()
ax = fig.add_subplot(111, polar=True)
c = ax.contourf(T.detach().numpy(), R.detach().numpy(), predicted.cpu().detach().numpy(), 50, cmap='viridis')
fig.colorbar(c)
plt.show()
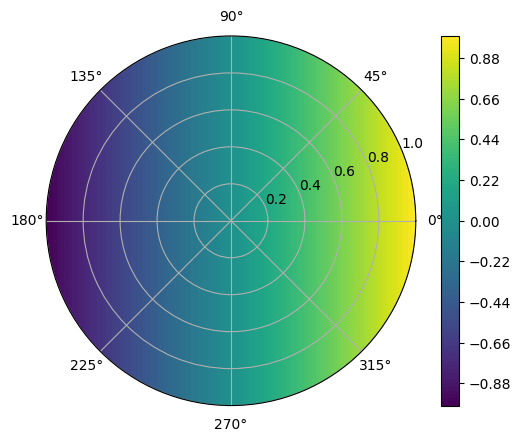
fig = plt.figure()
ax = fig.add_subplot(111, polar=True)
c = ax.contourf(T.detach().numpy(), R.detach().numpy(), analytic_cal.cpu().detach().numpy(), 50, cmap='viridis')
fig.colorbar(c)
plt.show()
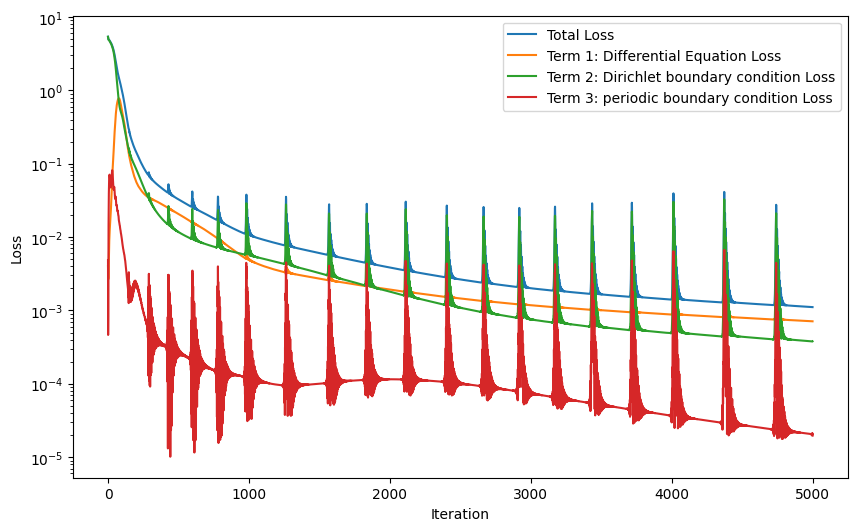
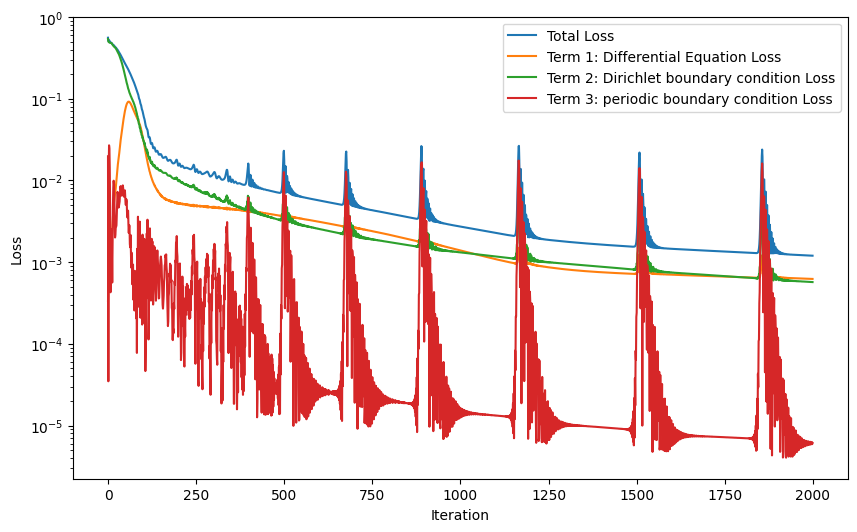
plt.figure(figsize=(10, 6))
plt.semilogy(L_total_history, label="Total Loss")
plt.semilogy(L_phy_history, label="Term 1: Differential Equation Loss")
plt.semilogy(L_BC1_history, label="Term 2: Dirichlet boundary condition Loss")
plt.semilogy(L_BC2_history, label="Term 3: periodic boundary condition Loss")
plt.xlabel('Iteration')
plt.ylabel('Loss')
plt.legend()
plt.show()
MSE error: 0.0494583323597908
پیادهسازی نهایی#
import torch
import torch.nn as nn
import matplotlib.pyplot as plt
from tqdm import trange
device = 'cuda' if torch.cuda.is_available() else 'cpu'
print(f"Your device is using {device}")
class NeuralNet(nn.Module):
def __init__(self, input_size, hidden_size, output_size):
super().__init__()
self.l1 = nn.Linear(input_size, hidden_size)
self.l2 = nn.Linear(hidden_size, hidden_size)
self.l3 = nn.Linear(hidden_size, hidden_size)
self.l4 = nn.Linear(hidden_size, output_size)
self.tanh = nn.Tanh()
def forward(self, x):
out = self.tanh(self.l1(x))
out = self.tanh(self.l2(out))
out = self.tanh(self.l3(out))
out = self.l4(out)
return out
class Trainer:
def __init__(self, model, optimizer, domain1, domain2, weights):
self.model = model
self.optimizer = optimizer
self.domain1 = domain1
self.domain2 = domain2
self.weights = weights
self.L_total_history = []
self.L_phy_history = []
self.L_BC1_history = []
self.L_BC2_history = []
def exact_solution(self, points):
r, t = points[:, 0:1], points[:, 1:2]
return r*torch.cos(t)
def grad(self, outputs, inputs):
return torch.autograd.grad(outputs, inputs, grad_outputs=torch.ones_like(outputs), create_graph=True)[0]
def generate_data(self, n_data):
t = torch.linspace(self.domain1[0], self.domain1[1], n_data)
r = torch.linspace(self.domain2[0], self.domain2[1], n_data)
R, T = torch.meshgrid((r, t), indexing="ij")
data = torch.vstack([R.ravel(), T.ravel()]).T.to(device)
return R, T, data
def loss_fn(self, u, dudr, d2udr2, d2udt2, points, indices1, indices2, indices3, weights):
w1, w2, w3 = weights
L_phy = w1*torch.mean((points[:, 0:1]*dudr + (points[:, 0:1]**2)*d2udr2 + d2udt2)**2)
L_BC1 = w2*torch.mean((u[indices1] - torch.cos(points[indices1, 1:2]))**2)
L_BC2 = w3*torch.mean((u[indices2] - u[indices3])**2)
loss = L_phy + L_BC1 + L_BC2
return loss, L_phy, L_BC1, L_BC2
def train(self, n_train, num_itr, show_itr=False):
R, T, points = self.generate_data(n_train)
points.requires_grad = True
indices1 = (points[:, 0]==1).nonzero(as_tuple=True)[0].to(device)
indices2 = (points[:, 1]==2*torch.pi).nonzero(as_tuple=True)[0].to(device)
indices3 = (points[:, 1]==0).nonzero(as_tuple=True)[0].to(device)
pbar = trange(num_itr)
for itr in pbar:
u = self.model(points)
dudr = self.grad(u, points)[:, 0:1]
d2udr2 = self.grad(dudr, points)[:, 0:1]
dudt = self.grad(u, points)[:, 1:2]
d2udt2 = self.grad(dudt, points)[:, 1:2]
loss, L_phy, L_BC1, L_BC2 = self.loss_fn(u, dudr, d2udr2, d2udt2, points, indices1, indices2, indices3, weights)
loss.backward()
optimizer.step()
optimizer.zero_grad()
self.L_total_history.append(loss.item())
self.L_phy_history.append(L_phy.item())
self.L_BC1_history.append(L_BC1.item())
self.L_BC2_history.append(L_BC2.item())
if show_itr and itr % 100 == 0:
print(f'iteration {itr}/{num_itr}, loss = {loss.item():.6f}')
else:
pbar.set_postfix({'loss': loss.item()})
def evaluation(self, n_test):
R, T, points = self.generate_data(n_test)
predicted = self.model(points.to(device))
analytic_cal = self.exact_solution(points).to(device)
mse = torch.mean((predicted - analytic_cal)**2)
print(f"MSE error: {mse}")
predicted = predicted.view(n_test, n_test)
analytic_cal = analytic_cal.view(n_test, n_test)
fig = plt.figure()
ax = fig.add_subplot(111, polar=True)
c = ax.contourf(T.detach().numpy(), R.detach().numpy(), predicted.cpu().detach().numpy(), 100,cmap='viridis')
fig.colorbar(c)
plt.show()
fig = plt.figure()
ax = fig.add_subplot(111, polar=True)
c = ax.contourf(T.detach().numpy(), R.detach().numpy(), analytic_cal.cpu().detach().numpy(), 100,cmap='viridis')
fig.colorbar(c)
plt.show()
plt.figure(figsize=(10, 6))
plt.semilogy(self.L_total_history, label="Total Loss")
plt.semilogy(self.L_phy_history, label="Term 1: Differential Equation Loss")
plt.semilogy(self.L_BC1_history, label="Term 2: Dirichlet boundary condition Loss")
plt.semilogy(self.L_BC2_history, label="Term 3: periodic boundary condition Loss")
plt.xlabel('Iteration')
plt.ylabel('Loss')
plt.legend()
plt.show()
Your device is using cuda
torch.manual_seed(42)
n_train, n_test, num_itr, itr_show = 30, 100, 5000, 1000
weights, domain1, domain2 = (5, 10, 1), (0, 2*torch.pi), (0, 1)
learning_rate = 0.001
input_size, hidden_size, output_size = 2, 30, 1
model = NeuralNet(input_size, hidden_size, output_size).to(device)
optimizer = torch.optim.Adam(model.parameters(), lr=learning_rate)
trainer = Trainer(model, optimizer, domain1, domain2, weights)
trainer.train(n_train, num_itr, show_itr=False)
trainer.evaluation(n_test)
100%|████████████████████████████████████████████████████████████████| 5000/5000 [01:15<00:00, 65.93it/s, loss=0.00111]
MSE error: 0.01583779789507389